
Ya puedes disfrutar del episodio 8 del podcast Biosíntesis [iVoox, iTunes, Google podcasts, Spotify, TuneIn, Radio Public, PlayerFM]. El episodio está fechado el 25 de septiembre de 2019, aunque se publicó el 02 de noviembre de 2019; fue grabado en el estudio de radio de la Facultad de Ciencias de la Comunicación de la Universidad de Málaga (UMA). Presentamos artículos científicos sobre bioquímica y biología molecular bajo la batuta de José (Pepe) Lozano @leviaingenia (Dep. Biología Molecular y Bioquímica, UMA), participamos Silvana Tapia @SilvanaTapia3 (Dep. Microbiología , UMA), y un servidor, Francisco R. (Francis) Villatoro, @emulenews (Dep. Lenguajes y Ciencias de la Computación, UMA). Así como bionoticias y anuncios gracias a Belén Delgado Martín, @bio_Belen (Graduada en Bioquímica, UMA) e Íker Puerto San Román, @SrMitocondrio (estudiante del Grado de Bioquímica, UMA), autor del blog La Mitocondria.
«En este episodio Francis nos comenta un análisis bioinformático publicado en Nature Microbiology que analiza la historia evolutiva de las agrupaciones génicas. Pepe entrevista a Sandra Peiró (VHIO, Barcelona) y comenta el último trabajo de su grupo, publicado en Oncogene, sobre una nueva estrategia terapéutica contra el cáncer de mama triple negativo. Silvana, por su parte, nos resume un interesante estudio comparativo en el que analizan la microbiota de los recién nacidos y nos presenta el libro «Superbacterias» (Editorial Guadalmazán) del microbiólogo José Ramos Vivas (IDIVAL, Santander), a quien entrevistamos en la última parte del episodio. Y, como siempre, nuestros estudiantes preferidos, Belén e Íker nos traen sus entetenidas (bio)noticias. Bienvenidos al octavo episodio de Biosíntesis».
En nuestra sección de reseñas con entrevista hemos reseñado el libro de José Ramos Vivas, «Superbacterias. ¿Qué son las superbacterias? ¿Vencerán las multirresistencias a los antibióticos? ¿Sucumbiremos ante las infecciones?» Guadalmazán (2019) [350 pp.].
Pepe empieza con sus efemérides habituales, para pedirme que hable de lo más destacado de Naukas Bilbao 2019 (que se celebró entre el jueves 19 y el domingo 22 de septiembre). Me toca ser el primero en presentar mi artículo seleccionado, el de Marina Marcet-Houben y Toni Gabaldón, ambos del Centro de Regulación Genómica (CRG), y de la Universitat Pompeu Fabra, Barcelona (España), que han publicado el 16 de septiembre de 2019 en la revista Nature Microbiology, titulado “Evolutionary and functional patterns of shared gene neighbourhood in fungi,” doi: https://doi.org/10.1038/s41564-019-0552-0. Más información divulgativa en “El genoma agrupa en regiones próximas los genes necesarios para algunas funciones”, Agencia SINC (16 sep 2019).
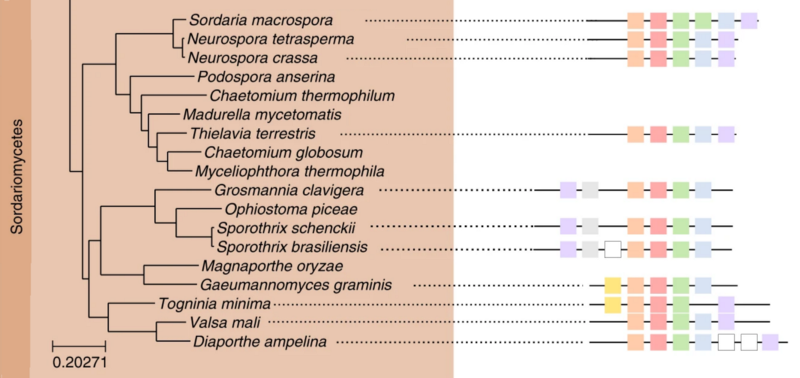
Se ha estudiado las agrupaciones de genes en los genomas en hongos (como ejemplo de eucariotas) que facilitan el despligue el ADN compactado en cromosomas para su expresión génica conjunta. Los genes próximos con función similar (como producir ciertas toxinas, como la penicilina) se corregulan de forma coordinada y más eficaz. Para desvelarlos se ha desarrollado un nuevo algoritmo bioinformática capaz de identificar estas agrupaciones de genes (gene clusters).

Se ha estudiado cómo evolucionan estas agrupaciones de genes (como la ilustrada en esta figura), tanto vía la evolución vertical, como la horizontal y la convergente. Se han observado 12 120 familias de agrupaciones de genes, con 118 699 agrupaciones individuales y 1 100 163 genes, en 341 genomas de hongos; estas agrupaciones representan el 32% de todos los genes de estos 341 genomas.
Se han estudiado las diferentes rutas evolutivas para estas agrupaciones de genes mediante la reconstrucción de sus árboles filogenéticos. Se ha observado que el 70% de las agrupaciones de genes están duplicadas al menos una vez en el linaje evolutivo; aunque las duplicaciones completas solo son el 5% (639).

Usando un algoritmo llamado EvolClassifier (cuyo organigrama se ilustra en la figura) se ha determinado si la evolución es vertical, horizontal (HGT) o convergente. Se han considerado dos conjuntos de datos: dataset50 y dataset75, según un umbral de confianza 50% y 75%, resp. Para el conjunto de datos dataset50 se ha observado un 69.5% de evolución vertical, un 26.2% de convergente y un 4.3% de horizontal. Para dataset75 se ha observado un 76.8% de evolución vertical, un 20.5% de convergente y un 2.7% de horizontal. También se ha estudiado la función de los genes en las agrupaciones usando las anotaciones de la Gene Ontology (GO).

Pepe nos presenta un artículo sobre cánceres de mama triple negativa publicado en la revista Oncogene por el grupo de Sandra Peiró, del Instituto de Oncología Vall d’Hebron (VHIO), Barcelona, cuyo primer autor es Joan Pau Cebrià-Costa; en concreto, J. P. Cebrià-Costa, L. Pascual-Reguant, …, S. Peiró, «LOXL2-mediated H3K4 oxidation reduces chromatin accessibility in triple-negative breast cancer cells,» Oncogene (28 Aug 2019), doi: https://doi.org/10.1038/s41388-019-0969-1. Como es habitual en las noticias de Pepe, se entrevista a Sandra, que nos presenta su trabajo de una forma exquisita.
Resumiendo mucho, se sabe que la compactación de la cromatina en los tumores de mama triple negativo es mayor que en otros cánceres. En el nuevo trabajo se ha encontrado una enzima que permite la descompactación, lo que facilita el ataque por agentes anticancerígenos. Dicha enzima es la lisil oxidasa LOXL2 que oxida la histona tres en la lisina 4 (H3K4ox). Aún siendo una investigación básica, parece que será fácil su traslación a la clínica.

Así llegamos a las bionoticias, que inicia Iker, que nos explica la noticia sensacionalista «¡Hallan una posible cura para el resfriado común!» yendo a su fuente, el artículo de Jonathan Diep, Yaw Shin Ooi, …, Jan E. Carette, «Enterovirus pathogenesis requires the host methyltransferase SETD3,» Nature Microbiology (16 Sep 2019), doi: https://doi.org/10.1038/s41564-019-0551-1. Como posible tratamiento contra las infecciones provocadas por enterovirus, entre los que se encuentran los rinovirus causantes del resfriado común, se propone buscar una molécula o péptido que impida la interacción de la proteína humana SETD3 con la proteasa 2A de estos enterovirus para tratar las infecciones causadas por estos virus.

Belén se hace eco de una noticia con un título muy curioso, Jon Cohen, «Microbe that got man drunk could help explain common liver disease,» News, Science (19 Sep 2019) doi: https://doi.org/10.1126/science.aaz5650, sobre el artículo de Jing Yuan, Chen Chen, …, Di Liu, «Fatty Liver Disease Caused by High-Alcohol-Producing Klebsiella pneumoniae,» Cell Metabolism 30: P675-688.E7 (01 Oct 2019), doi: https://doi.org/10.1016/j.cmet.2019.08.018. La autora principal del artículo es la microbióloga Jing Yuan, del Instituto de Pediatría de la Capital, en Pekín, China.
Se discute el papel de la microbiota en las enfermedades hepáticas de origen no alcohólico gracias a unas bacterias identificadas en el intestino de un chino que se «emborrachaba» hasta desmayarse sin tomar ni una gota de alcohol, solo tomando comidas con alto contenido en carbohidratos y azúcares. El síndrome de intoxicación que sufrió se asoció a la microbiota; así, en ratones estériles, se logró identificar las bacterias Klebsiella pneumoniae, que metabolizan el azúcar produciendo alcohol, como la causa última de las borracheras no alcohólicas. Se cree que esta bacteria tiene un rol relevante en las enfermedades hepáticas asociadas al hígado graso que no están relacionadas con el consumo de alcohol.
En las noticias breves, Belén nos cuenta la noticia de Nuño Domínguez, «Revuelta por el ninguneo de la ciencia en Europa. Miles de científicos, incluidos 17 premios Nobel, exigen que la investigación y la educación vuelvan al escalafón más alto de la Comisión Europea,» Materia, El País, 25 sep 2019. También nos cuenta la publicación del «Informe anual 2019 del Acuerdo de transparencia sobre el uso de animales en experimentación científica en España,» Cosce, 17 sep 2019.

Silvana nos presenta un estudio sobre la microbiota en neonatos que han nacido por parto vaginal y por cesárea de Yan Shao, Samuel C. Forster, …, Trevor D. Lawley, «Stunted microbiota and opportunistic pathogen colonization in caesarean-section birth,» Nature 574: 117-121 (18 Sep 2019), doi: https://doi.org/10.1038/s41586-019-1560-1; también recomiendo Andrea Du Toit, «Establishing the gut microbiota after birth,» Nature Reviews Microbiology 17: 647 (24 Sep 2019), doi: https://doi.org/10.1038/s41579-019-0276-4. Se observa una gran variabilidad en la microbiota neonatal resultado de la colonización por patógenos oportunistas asociados al entorno hospitalario.

Destaca el contenido de bacterias resistentes a los antimicrobianos que pueden colonizar al neonato en el hospital; este factor de riesgo ha sido subestimado en los estudios previos y debe ser considerado. Además, las microbiotas de los neonatos evolucionan rápido con el tiempo, con lo que las diferencias iniciales entre el parto vaginal y por cesárea se diluyen, con lo que al cabo de unos meses hay pocas diferencias entre ambos. Aún así se podrían usar tratamientos con probióticos para moldear una evolución óptima.

Finalmente, en nuestra sección de reseñas y entrevistas tenemos a José Ramos Vivas, «Superbacterias. ¿Qué son las superbacterias? ¿Vencerán las multirresistencias a los antibióticos? ¿Sucumbiremos ante las infecciones?» Guadalmazán (2019) [350 pp.]. Un libro muy necesario sobre la “crisis de los antibióticos”, un problema de salud global que se discute desde múltiples perspectivas (microbiológica, sanitaria, ecológica, económica…). Según nos cuenta el autor, «hemos de conseguir que la gente lea [este libro] para que sea consciente de [este grave problema] desde una perspectiva científica, alejada del alarmismo con el que su magnitud obliga a los medios y redes sociales a tratar este tema tan complejo».
¡Qué disfrutes del podcast!

