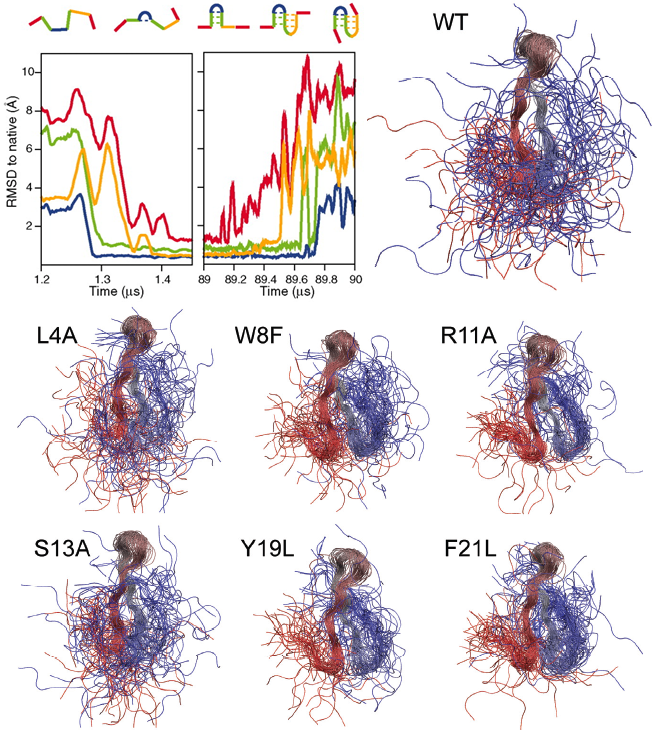
David Shaw, informático y especialista en supercomputadores, desarrolló algoritmos para inversión bursátil en Wall Street. Tuvo tanto éxito que fundó su propia hedge fund y alcanzó un puesto en la lista Forbes de los 400 hombres más ricos de EE.UU. Aburrido con las finanzas decidió retornar a la ciencia, la biología computacional. Ha diseñado un supercomputador de propósito específico para el estudio del plegamiento de proteínas. Hoy publica en la revista Science su primer gran éxito, Anton, un supercomputador de propósito específico (fabricado por su compañía D.E. Shaw Research o DERES) que es 100 veces más rápido que el supercomputador de propósito general más rápido del mundo. Eso sí, 100 veces más rápido en la única tarea que sabe hacer, estudiar el plegamiento de una proteína. Anton es un supercomputador con 512 procesadores diseñado para acelerar las simulaciones de dinámica molecular, la determinación de las interacciones entre los átomos de una proteína, y ha sido capaz de estudiar la evolución de 13564 conformaciones de una pequeña proteína (FiP35), con 35 aminoácidos, y seis de sus mutaciones. David Shaw y sus colegas han fabricado 11 copias de este supercomputador con 512 procesadores (uno de ellos ha sido donado al Centro de Supercomputación Biomédica de Pittsburgh, Pennsylvania, EE.UU.). El objetivo de Shaw es fabricar una nueva máquina con 1024 procesadores y diseñar una máquina futura con 2048. Shaw, tras su retorno a la ciencia ha afirmado: «Me encanta esto. Es la cosa más divertida que he hecho jamás. Es muy satisfactorio para mí» [«I love this. It’s just the most fun I’ve ever had. It’s very satisfying«]. Nos lo ha contado Robert F. Service, «Computational Biology: Custom-Built Supercomputer Brings Protein Folding Into View,» News of the Week, Science 330: 308-309, 15 October 2010. El artículo técnico, para los interesados en más detalles, es David E. Shaw et al., «Atomic-Level Characterization of the Structural Dynamics of Proteins,» Science 330: 341-346, 15 October 2010. Abajo, el plegamiento de una cadena de 6 aminoácidos (arriba, izquierda), la forma final de la proteína FiP35, llamada WT (arriba, derecha), y la forma final de los 6 mutantes estudiados (abajo). Estas proteínas fueron seleccionadas porque son pequeñas y porque su plegamiento es uno de los más rápidos conocidos (uno de los más difíciles de estudiar). El artículo técnico será de interés para todos los interesados en el plegamiento de proteínas, que no son pocos en España y en el resto del mundo.
3 Comentarios
Deja un comentario
Por Francisco R. Villatoro, publicado el 15 octubre, 2010
Categoría(s): Biología • Ciencia • Informática • Noticias • Science
Etiqueta(s): Biología, Biología molecular, Ciencia, Curiosidades, dinámica molecular, Física computacional, Informática, Matemática aplicada, Noticias, Plegamiento de proteínas, Supercomputadores
⇦ XII Carnaval de la Física: El frigorífico de Einstein-Szilard y el experimento para medir el espín del electrón de Einstein-de Haas • Los alucinantes bailes de las burbujas ⇨
Categoría(s): Biología • Ciencia • Informática • Noticias • Science
Etiqueta(s): Biología, Biología molecular, Ciencia, Curiosidades, dinámica molecular, Física computacional, Informática, Matemática aplicada, Noticias, Plegamiento de proteínas, Supercomputadores
⇦ XII Carnaval de la Física: El frigorífico de Einstein-Szilard y el experimento para medir el espín del electrón de Einstein-de Haas • Los alucinantes bailes de las burbujas ⇨



“Antón, Antón,
Antón Pirulero,
cada cual, cada cual
que atienda su juego,
y el que no lo atienda,
pagará una prenda”.
Quicir, ¿una nueva competición dentro de la biologia, à la genoma humano ?
Otros proyectos, académicos, con objetivos similares utilizan, en vez de la computación paralela, la computación distribuida con redes de cientos de miles de computadores, por ejemplo
http://folding.stanford.edu/English/Papers
o
http://www.systemsbiology.org/Scientists_and_Research/Technology/Data_Visualization_and_Analysis/Human_Proteome_Folding_Project.
El problema de plegamiento de proteinas refleja muy bien la actual complejidad de los problemas científicos:
–desde el punto de vista teorico sabemos que algunos modelos abstractos de este problema son NP-completo (ver por ejemplo: http://www.csc.liv.ac.uk/~ped/teachadmin/COMP202/annotated_np.html , problema 86)
–para quien el dato asíntotico peor caso diga poco (cómo a mi), quizás lo entienda mejor sabiendo que existen unas 20-30000 proteinas humanas (y unas 7.400.000 secuenciadas humanas o no humanas), que el tamaño medio de la proteina humana es de unos 480 aminoacidos (fuente NCBI) y que en 2006, si para encontrar una estructura terciaria solución de una cadena de 20 aminoacidos se necesitaban 20 dias de CPU, resolver una cadena de 60 aminoacidos requería 8000 dias de CPU. (fuente: http://www.biomedcentral.com/content/pdf/1472-6807-7-12.pdf) y me temo que el estado del arte no ha progresado mucho en estos tres años.
Por ello bienvenida sea la competición. Una duda: ¿Son patentables las estructuras terciarias de proteinas ?
Realmente son muchas más las proteinas cuya secuencia es conocida. El tamaño típico está entre 50 y 2000 residuos o amino ácidos. Ver pags. 3 y 4 de la tesis (ya algo antigua):
http://onlinelibrary.wiley.com/doi/10.1002/prot.22589/pdf
También hay mucha más competición de la que pensaba y organizada, tipo SAT solvers. Ver los CASP (Critical assessment of protein structure prediction) en:
http://predictioncenter.org/index.cgi
Perdón el enlace de la tesis es:
http://lars.malmstroem.net/lars.malmstroem.thesis.no_articles.pdf