
Los fractales son objetos matemáticos ideales que son autosemejantes (que se repiten así mismos) a todas las escalas (ad infinitum). Por ello, los fractales no existen en la Naturaleza; solo se observan prefractales, autosemejantes en un número finito (y pequeño) de escalas. Ello no resta belleza a objetos como los meristemos florales hipertrofiados y carnosos de la coliflor y del romanesco. Se ha publicado en Science el posible origen genético de dicha autosemejanza usando experimentos y modelos computacionales. Se ha encontrado una red de varios genes, llamada SALT, que se expresan en diferentes lugares del meristemo dando lugar a la estructura espiral prefractal de las coliflores; además, se ha identificado un gen, CLAVATA3 (o CLV3), como probable responsable de la forma cónica de los meristemos de los romanescos, que explicaría su bella estructura prefractal. Me ha gustado que se usen sistemas L (Lindenmayer) acoplados a las ecuaciones diferenciales de la red de genes en el modelo computacional desarrollado.
El romanesco es una variedad de la cloliflor (Brassica oleracea var. botrytis), la misma especie a pesar de su aspecto. Por ello, su estructura prefactal tiene el mismo origen que la de la coliflor, una estructura de espirales anidadas a varias escalas (como la mostrada en la figura de arriba al colorear la superficie floral de forma adecuada). Su origen es la filotaxis espiral de los meristemos apicales de los brotes florales, que también originan el capítulo de las flores (girasol o margarita), o los conos de los pinos (piñas), por poner otros dos ejemplos. La red de genes SALT, por las siglas de sus genes SAX, AP1/CAL, LFY y TFL1, se ilustra en la figura (en la parte de abajo, a la izquierda); recuerda que en ella las flechas indican activación (promoción) y la flechas con punta en T indican desactivación (represión). En la red actúan como señales externas la fitohormona auxina, promotora de LFY, una señal de inducción de la floración llamada F, que representa varios promotores de AP1/CAL y SAX, y un represor de TFL1 llamado eREP. En los experimentos in vivo con Arabidopsis thaliana se ha usado la técnica CRISPR-Cas9 para desarrollar mutantes con los que estudiar in vivo el rol de la red SALT.
El artículo es Eugenio Azpeitia, …, Francisco Madueño, …, François Parcy, «Cauliflower fractal forms arise from perturbations of floral gene networks,» Science 373: 192-197 (09 Jul 2021), doi: https://doi.org/10.1126/science.abg5999 (recomiendo consultar la información suplementaria con el modelo dinámico de la red de genes y la arquitectura del sistema L usado); varios medios se hicieron eco de este artículo, como Laura Elizabeth Lansdowne, «Unraveling the Romanesco Cauliflower’s Spiraling Structure», Technology Networks, Genomics Research (21 Jul 2021) [web]; Nikk Ogasa, «How Romanesco cauliflower forms its spiraling fractals,» Science News, 08 Jul 2021 [web].

Una red con cuatro bloques de genes involucrados en varios ciclos de realimentación positiva y negativa es difícil de explicar en detalle; permíteme un resumen muy breve (siguiendo la explicación del artículo en Science, al que remito para más detalles). En Arabidopsis, el regulador principal del momento de desarrollo floral y del surgimiento de un meristemo de inflorescencia es el gen TFL1 (TERMINAL FLOWER 1), cuya proteína reprime el gen LFY (TF LEAFY). LFY está regulado por dos factores de transcripción tipo MADS-box, llamados SOC1 (SUPPRESSOR-OF-OVEREXPRESSION-OF-CO 1) y AGL24 (AGAMOUS-LIKE), y por la fitohormona auxina (Auxin). En el meristemo apical de los brotes TFL1 reprime a LFY; pero en el primordio floral, LFY induce AP1 (APETALA1) y CAL (CAULIFLOWER), en un bucle realimentado positivo con LFY, y reprime SOC1/AGL24 y TFL1, logrando que el nuevo meristemo acabe en una flor. En el estudio in vivo se ha usado un mutante ap1/cal que carece del bucle realimentado positivo y en el que TFL1 no está reprimido por AP1/CAL.
En el nuevo artículo se han buscado nuevos reguladores de TFL1 (además de LFY); se ha encontrado que la longitud del día regula TFL1, de hecho, en los días largos TFL1 está regulada por CO (CONSTANS) y FT (FLOWERING LOCUS T). Además, se ha observado que los tres genes SOC1, AGL24 y XAL2 (XAANTAL2), resumidos en el término SAX, son reguladores positivos de TFL1. Finalmente, se ha añadido F (un proxy del florigen FT), como señal que induce la floración y que presenta un valor umbral. Todos ellos se han incorporado en el nuevo modelo SALT.

El resultado es la red de genes SALT (siglas de SAX, AP1/CAL, LFY y TFL1), cuyas ecuaciones muestro por simple curiosidad; en ellas se ha usado la cinética regida por la ley de Hill, tanto para regulación positiva, X/(k+X), como para la negativa, k/(k+X). En estas ecuaciones S, A, L, T, aux, D y R representan SAX, AP1, LFY, TFL1, auxin, el dímero SAX-AP1 y el represor eREP de TFL1, respectivamente. Para el resto de los parámetros y constantes, remito a la información suplementaria.
En este tipo de modelos se estudia el estado estacionario (homeóstasis) para los diferentes estados de interés en los meristemos apicales: si F está por debajo de su umbral serán estados vegetativos (bajos valores de SALT y F por debajo de su umbral) y si F está por encima del umbral serán inflorescencias (altos valores de TLF1/SAX y bajos de AP1/CAL/LFY) o flores (bajos valores de TLF1/SAX y altos de AP1/CAL/LFY). Los resultados de las simulaciones computacionales de esta red de regulación génica (GRN) muestran buen acuerdo con la dinámica esperada.
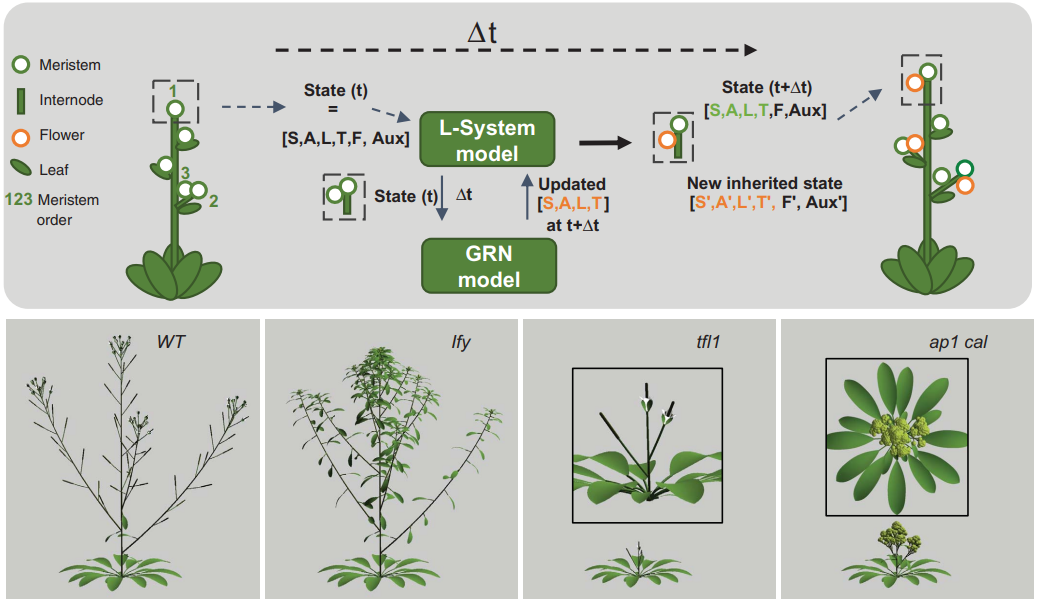
Para estudiar el efecto de la GRN SALT sobre el crecimiento de las plantas, me ha llamado la atención que se haya usado un modelado con sistemas L. Lindenmayer (1968) introdujo un método basado en gramáticas formales (que se usan en ciencias computacionales para describir la ortosintaxis de los lenguajes de programación, necesarios para desarrollar compiladores o intérpretes); los sistemas L se pueden usar para describir objetos fractales, pero su nicho respecto a otras técnicas ha sido siempre la representación gráfica de plantas (en 1996 presenté en las II Jornadas de Informática un trabajo sobre este tema, «Representación de árboles mediante L-gramáticas y sistemas de partículas»). Así, la gramática del sistema L describe las reglas simbólicas (gramaticales, valga la redundancia) del crecimiento de la planta.
En este artículo en Science se acopla el sistema L con el modelo compartimental SALT, de tal forma que a cada paso de tiempo de la simulación dinámica se aplican las correspondientes reglas gramaticales y se dibujan los elementos correspondientes de las plantas. Así se realizan experimentos in silico del crecimiento de plantas y de su floración, cuyos resultados se validan con los experimentos in vivo.

El artículo ha puesto especial atención al origen de la estructura cónica prefractal en el romanesco. Se ha usado la secuenciación de transcriptoma completo (técnica RNA-seq) para identificar las diferencias en la expresión de genes entre la coliflor y el romanesco. Se observan variaciones en (i) el plastocrón, el tiempo entre la producción sucesiva de dos meristemos, (ii) el número de espirales visuales que se originan en cada meristemo, (iii) el tiempo (medido en número de plastocronos) antes de que un primordio comience a producir su propios primordios (es decir, el retraso en el inicio de la producción lateral), y (iv) el tamaño de los meristemos. Según el artículo en Science no está claro si algunos de estos parámetros es la causa última del fenotipo romanesco; pero los estudios de filotaxis apuntan a que los tres primeros parámetros están relacionados con el tamaño del meristemo. Así lo confirma in silico una versión simplificada del modelo multiescala desarrollado.

En este figura se muestra la expresión génica de varios genes en tres coliflores y tres romanescos; la diferencia más destacada se observa en el gen BobCLV3 (al nombre del gen CLV3 (CLAVATA3) se le añade Bob por la especie Brassica oleracea (Bo) var. botrytis (Bob)). Así se propone como hipótesis más prometedora para explicar el romanesco una mutación en el gen CLV3 controla la homeostasis del meristemo que da lugar a la estructura cónica prefractal del romanesco. Para verificar la hipótesis se ha desarrollado un mutante clv3 con CRISPR-Cas9. Los resultados apoyan la hipótesis, pero no se debe cerrar la puerta a que otras mutaciones en otros genes también jueguen un papel relevante.
En resumen, conocer el origen genético de la belleza fractal de las plantas me parece muy interesante, por ello he rescatado este trabajo que se publicó en julio. Por desgracia, aunque se ha desvelado una red de genes que la explica para la coliflor y una mutación que podría explicar las peculiaridades del romanesco, todavía no se puede afirmar que sean la respuesta definitiva. Seguro que hay otros genes y otras mutaciones involucrados que serán desvelados en futuro; habrá que estar al tanto de los progresos en este área.


Preciosos ambos artículos, el de Science y tu entrada Francis.
Aunque autosimilaridad y fractalidad a menudo están ligadas, no son lo mismo.
Un fractal es un objeto con una dimensión de Hausdorff superior a su dimensión topológica.
Hay fractales no autosimilares y objetos autosimilares no fractales (una línea, sin ir más lejos)
Un saludo,
Juan Carlos—
@ApuntesCiencia
Interesante artículo. Mi tesis casi fue, pero no, en L-systems y arquitectura de Arabidopsis (pero no arquitectura floral)
Hay un montón de trabajos ahora que usan los Lindenmayer system para modelar filotaxis, pero en particular el discípulo de Lindenmayer, Prusinkiewicz en Calgary y Godin en el Virtual Plants labs del INRIA (los que hicieron L-py, el paquete que usaron aquí). Hay un paquete menos conocido, pero que parece que ayuda a implementar redes de regulación genética y L-systems – http://www.transsys.net y que este verano ví al autor en una conferencia y prometía que lo estaba actualizándolo. Y luego todo el trabajo que hay de tras de los FSPM (functional structural plant models) como la infraestructura https://github.com/openalea
A mi lo que aún me cuesta comprender es como afinan los parámetros para conseguir la estructura deseada con el L-system.
Un ejemplo con la planta completa de Arabidopsis
Mundermann, L., Erasmus, Y., Lane, B., Coen, E., & Prusinkiewicz, P. (2005). Quantitative modeling of Arabidopsis development. Plant physiology, 139(2), 960-968.
Saludos.
Me encánta. Gracias.